Finally, kita sampai di
penghujung pembahasan terkait PNN dan CPNN. Yeaaay!
Berikut merupakan script R untuk
menghitung probabilitas kelas bersyarat dengan menggunakan PNN dan CPNN.
Pembahasan PNN dan CPNN berikut algoritma yang digunakan dalam script ini mengacu pada penelitian yang
dilakukan oleh Zeinaly dan Story (2017) dan dibuat oleh Pak Hastu tanpa
mengubah petunjuk dan arahan yang bapak berikan, hanya menambahkan sedikit keterangan
tambahan dan link untuk memahami
format fungsi R-nya lebih lanjut. Kalimat
yang saya cetak tebal (bold)
merupakan tambahan keterangan dari saya. Saya akan coba jelaskan secara garis
besar maksud dan alur berpikir dari script
yang saya lampirkan berikut ini, ya! Sekaligus akan saya sertakan juga
contoh datanya, jadi kalian langsung download juga.
Berikut ini merupakan script PNN dan CPNN beserta dengan penjelasannya
# Ini script pnn dan cpnn yang
aku bikin tanpa menggunakan paket dari R
# atau dengan kata lain, dibuat
dari awal, mengacu pada paper zeinali
# Buat dipelajari, ada baiknya
jangan dijalankan langsung, tapi baris demi baris saja dulu
# Setelah itu, tekan cntrl+enter,
maka R akan mengeksekusi sebuah instruksi di baris bawahnya
# Lakukan hal ini sampai baris
paling bawah, sambil dipelajari kira2 apa maksud script yg aku
# sudah aku tulis ini
#Sama seperti mengetikkan “reinit” di GrADS atau “clear all” di
Matlab, remove list -> rm(list) di
R memiliki peranan yang serupa, yaitu
untuk menghapus semua objek atau membersihkan workspace pada menu entri sehingga
program kembali ke kondisi “default”, kondisi awal, dimana belum ada fungsi
yang aktif, belum ada data yang dipanggil, dan lain-lain. Sehingga tidak ada
fungsi atau command yang tumpang
tindih nantinya. Sementara itu, penjelasan yang lebih lengkap mengenai
dev.list dan dev.off dapat kalian
baca di link ini.
rm(list = ls())
while(!is.null(dev.list()))
dev.off()
# Pastikan di R mu sudah terinstal
paket dplyr. kalau baris nomer 18 ini error
# Saat dijalankan, itu berarti
paket dplyr belum ada di komputermu.
# Untuk menginstal paket ini bila
belum ada, caranya:
# 1. pastikan komputermu terhubung
ke internet
# 2. ketik
install.packages('dplyr') di bagian console (di bawah script script editor ini)
# Setelah itu jalankan kembali bari
nomer 18 ini
# Di sebagian device, termasuk di punya saya ketika saya mengetikkan library(dplyr) maka muncul peringatan
berikut.
Attaching package: ‘dplyr’
The following objects are
masked from ‘package:stats’:
filter, lag
The following objects are
masked from ‘package:base’:
intersect, setdiff, setequal, union
# Peringatan tersebut setelah saya baca artinya bahwa kedua packages memiliki fungsi dengan nama
yang sama. Dalam kasus ini, dplyr
dengan stats memiliki 2 fungsi yang
sama serta dplyr dengan base memiliki 4 fungsi yang sama. Jika
memang terganggu dan tidak ingin peringatan tersebut muncul kembali, kalian bisa mengetikkan library(dplyr, warn.conflicts=false).
library(dplyr)
# Fungsi di bawah ini digunakan untuk menghitung
jarak Euclidian antara nilai 1 dan nilai
2. Fungsi rbind digunakan untuk menggabungkan data by row (berdasar baris) antara nilai 1 dan 2, kemudian baru
dihitung jarak Euclidnya dengan fungsi dist. Penjelasan lebih lanjut untuk
fungsi dist dapat kalian lihat di link berikut,
sementara untuk rbind di link berikut.
Ohiya, bagi yang sama kayak aku penasaran sama maksud simbol ini %>%, jadi
simbol tersebut sangat identik digunakan ketika kita menggunakan
library(dplyr), jadi kayak udah pasangan gitu mereka berdua. Ketika kita tidak
memanggil library(dplyr) maka kita tidak mungkin bisa mengeksekusi command di
bawah ini.
jarak.kuadrat <-
function(nilai.1, nilai.2) nilai.1 %>% rbind(nilai.2) %>% dist %>%
'^'(2)
# Setelah menghitung jarak Euclid, kemudian
menghitung nilai kernel (omega.ij) dengan data input baru (x.new), data yang
sudah ada (x.cij) dengan spread parameter
(sigma.input). Perhitungan ini persis seperti rumus yang tertera dalam paper
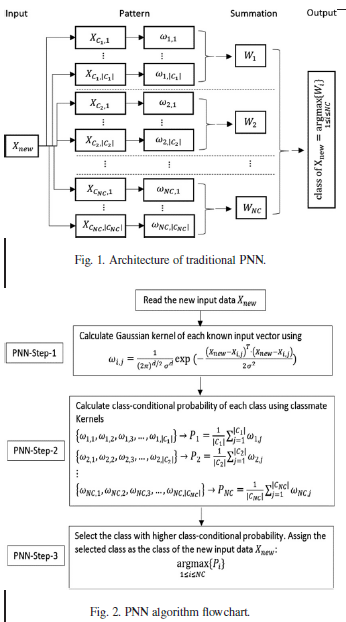
Zeinali dan Story (2017) dan sudah dijelaskan pada postingan sebelumnya.
omega.ij <- function(x.new,
x.c.ij, sigma.input) {
argumen <- -jarak.kuadrat(x.new, x.c.ij) %>% '/'(2 *
(sigma.input^2)) %>% exp
return(argumen / (
((2 * pi)^(length(x.new) / 2)) *
(sigma.input^length(x.new))
)
)
}
# Setelah mendapatkan nilai kernel untuk
tiap data, maka dilanjutkan dengan menghitung probabilitas kelas bersyarat (class-conditional probability,
p.x.new.ci), dimana gamma.input tidak diperhitungkan dalam PNN dan
diperhitungkan nilainya dalam CPNN. Fungsi p.x.new.ci
digunakan untuk menghitung nilai class-conditional
probability, sementara jumlah.omega
dihitung dengan mempertimbangkan nilai dari gamma.input
untuk menyeleksi seberapa banyak data.input
yang dipertimbangkan dalam perhitungan. Kemudia nilai kernel yang terpilih
diurutkan dengan fungsi sort dari
urutan yang terbesar ke terkecil (rev).
Setelah itu, sama seperti perhitungan dalam algoritma PNN, nilai tersebut
dihitung rata-ratanya (mean).
p.x.new.ci <- function(x.new,
data.input, sigma.input, gamma.input = NULL) {
if(!is.null(gamma.input) & is.numeric(gamma.input)) {
jumlah.omega <- data.input %>% nrow
%>% '*'(gamma.input) %>% round
omega <- apply(data.input, 1,
function(input1)
omega.ij(x.new, input1, sigma.input))
%>% sort %>% rev
return(omega[1:jumlah.omega] %>%
mean(na.rm = TRUE))
} else {
apply(data.input, 1, function(input1)
omega.ij(x.new, input1, sigma.input))
%>% mean(na.rm = TRUE)
}
}
# Pada algoritma CPNN, fungsi di atas
selanjutnya diterapkan pada “kelas terpilih” SAJA yang ditentukan berdasarkan gamma.input dan untuk dapat melakukan penerapan
fungsi pada bagian yang terpilih maka digunakan fungsi tapply(X, index, fun), dimana X
adalah objek (vektor), index adalah list yang mengandung vektor, dan fun adalah fungsi yang ingin diterapkan.
Selanjutnya juga terdapat sapply yang memiliki fungsi yang sama dengan lapply
namun dapat digunakan untuk kembali ke perhitungan vektor. Penjelasan lebih
lanjut mengenai fungsi ini dapat dilihat melalui link berikut. Kemudian sebagai output, kelas ditentukan
berdasarkan nilai Parzen yang terbesar (which.max)
c.pnn <- function(x.new,
data.input, data.kelas, sigma.input, gamma.input = NULL) {
indeks.kelas <- tapply(1:length(data.kelas), data.kelas,
function(input1) return(input1))
hasil.p.x.new.ci <- sapply(
indeks.kelas, function(input1) {
p.x.new.ci(x.new, data.input[input1, ],
sigma.input, gamma.input)
}
)
output <- data.frame(
kelas = (data.kelas %>% as.factor %>%
levels)[hasil.p.x.new.ci %>% which.max],
nilai.parzen.terpilih =
hasil.p.x.new.ci[hasil.p.x.new.ci %>% which.max]
)
rownames(output) <- NULL
return(output)
}
# Baris-baris script di atas adalah
fungsi2 untuk melakukan proses perhitungan
# PNN dan CPNN. kedua algoritma
tersebut dipanggil menggunakan fungsi yang sama,
# yaitu c.pnn(). yang membedakan
adalah: untuk pnn, parameter gamma tidak usah diisi,
# atau diisi dengan 'NULL',
sedangkan untuk melakukan proses perhitungan cpnn,
# Parameter gamma diisi dengan
angka real 0 s/d 1.
# Implementasi pada contoh data
adalah sbb:
# Buka filenya
# Pastikan mengisi dengan lengkap
nama direktorinya juga, di dalam tanda petik,
# Misalnya:
# 'D:/skripsi/contohdata.csv'
# Tapi karena di komputerku sudah
aku set direktorinya, jadi tdk perlu aku tambahkan
# Kalau di komputermu, tambahkan
nama direktorinya
contoh.data <- read.csv('D:/contohdata.csv',
sep = ';')
# Standardisasi fitur-fiturnya
kecuali fitur respon
# Seperti yang kita ketahui bahwa syarat
perhitungan dengan PNN dan CPNN, prediktor yang dimiliki harus distandardisasi
atau dinormalisasi. Dalam R, perhitungan ini dilakukan dengan menggunakan
fungsi scale, KECUALI pada kolom VINTAGES karena merupakan variabel respon
dalam kasus ini
contoh.data.scale <-
scale(contoh.data %>% select(-vintages))
# Ambil beberapa contoh data untuk
dicoba, misalnya sejumlah 10
# Sebelum digunakan untuk menguji data
diluar data training, maka perlu dicoba dulu untuk menguji beberapa sampel dari
training data itu sendiri. Ketika hal ini dilakukan, kita dapat mengetahui
apakah model kita underfitting atau overfitting. Command selanjutnya
insyaAllah lebih mudah dimengerti dan sudah disertai dengan keterangan yang
sudah cukup membantu, ya kan?
indeks.coba <-
sample(1:nrow(contoh.data.scale), 10, replace = FALSE)
# Pisahkan data training dengan
testing
training <-
contoh.data.scale[-indeks.coba,]
testing <-
contoh.data.scale[indeks.coba,]
# Buat daftar respon training dan
testing sesuai uruta pengambilan acak
respon.training <-
contoh.data$vintages[-indeks.coba]
respon.testing <-
contoh.data$vintages[indeks.coba]
# Coba kita lihat hasilnya
head(training, 30)
View(testing)
head(respon.training, 30)
View(respon.testing)
# Sekarang kita coba menjalankan
pnn dg nilai sigma = 0.7
hasil.pnn <- apply(
testing, 1, function(input) {
c.pnn(x.new = input,
data.input = training,
data.kelas = respon.training,
sigma.input = 0.7)
}
)
# Sekarang kita coba menjalankan
cpnn dengan nilai sigma 0.7 dan nilai gamma 0.9
hasil.cpnn <- apply(
testing, 1, function(input) {
c.pnn(x.new = input,
data.input = training,
data.kelas = respon.training,
sigma.input = 0.7,
gamma.input = 0.9
)
}
)
# Sekarang lihat hasil pnn:
(hasil.pnn)
# Sekarang lihat hasil cpnn:
(hasil.cpnn)
# Sekarang kita lihat confussion:
# Fungsi table disini adalah untuk membuat tabel dengan respon.testing sebagai row dan hasil sapply sebagai kolom dengan format karakter (as.karakter). Penjelasan lebih lanjut terkait tabel dapat kit abaca
melalui link berikut.
conf.pnn <-
table(respon.testing %>% as.character,
sapply(hasil.pnn,
function(input) input$kelas) %>% as.character)
# Sekarang kita lihat confussion:
conf.cpnn <-
table(respon.testing %>% as.character,
sapply(hasil.cpnn,
function(input) input$kelas) %>% as.character)
# Tampilkan hasilnya:
(conf.pnn)
(conf.cpnn)
Jadi seperti itulah, script PNN dan CPNN. Catatan:
INGAAT! untuk semua tulisan yang bold harus dihapus terlebih dahulu ya sebelum
mengeksekusi script ini di R. Semoga tulisan ini bisa bermanfaat dan mohon
doanya agar tugas akhirku dapat diselesaikan dengan baik, yaa! See you next
time! Hehe.